Eintausend Pflanzen-Transkriptomprojekt trägt Früchte
Neue Einblicke in die Evolution der Landpflanzen
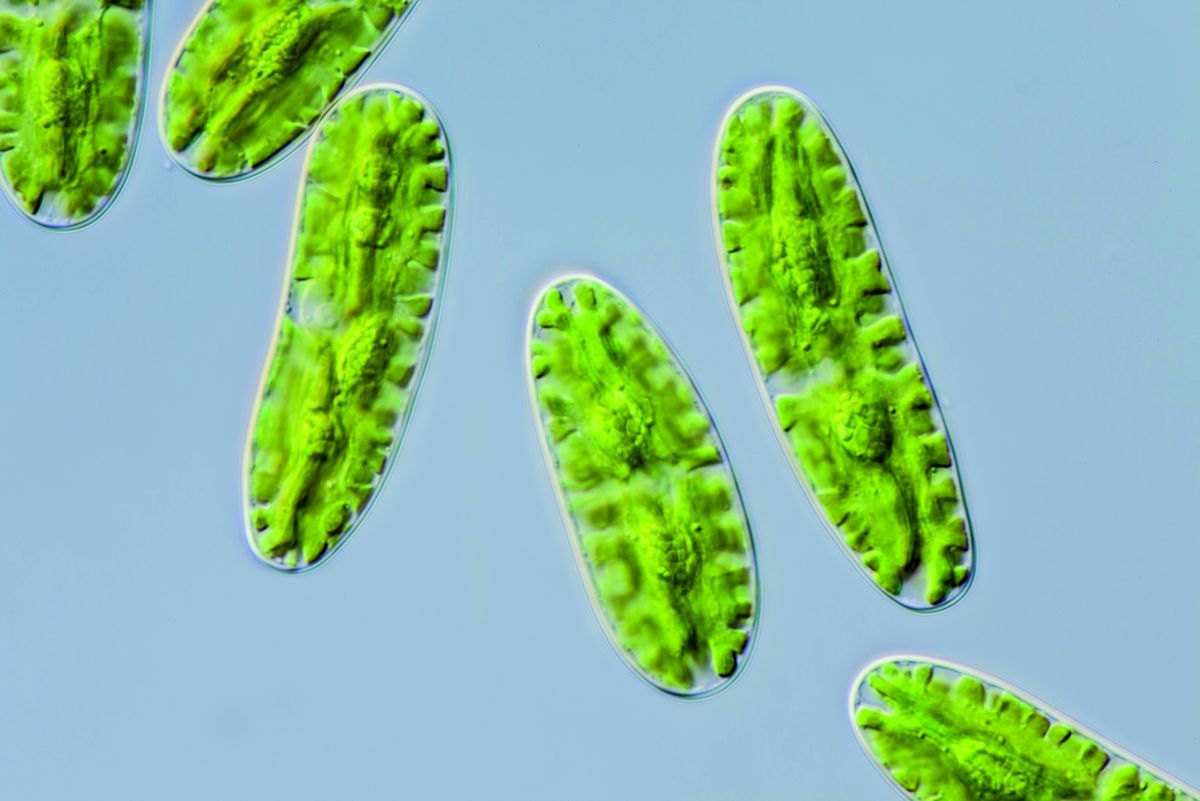
Lichtmikroskopische Aufnahme der einfachen, einzelligen Alge Netrium oblongum. Netrium oblongum gehört zur Gruppe der Algen, die am nächsten mit den heutigen Landpflanzen verwandt sind. (Bildquelle: © Michael Melkonian, Universität zu Köln)
Vor etwa 450 Millionen Jahren haben Pflanzen ihren Weg aus dem Wasser aufs Land gefunden. Wissenschaftler haben nun genetische Daten von Hunderten verschiedener Pflanzenarten verglichen und neue Erkenntnisse über ihren Verwandtschaftsgrad gewonnen.
Ein internationales Konsortium hat in einer groß angelegten Studie neue Einblicke in die Evolution der Pflanzen gewonnen. Das „Eintausend Pflanzen-Transkriptomprojekt (1KP)“ verfolgt das Ziel, von 1.000 Pflanzenarten, darunter etwa 200 Algenarten, Millionen von Gensequenzen zu ermitteln. Diese Gensequenzen dienen als Grundlage für Stammbaumanalysen und bioinformatische Methoden, mit deren Hilfe sich unter anderem die Entstehung der heutigen Landflora zurückverfolgen lässt.
Wertvolle Algensammlung

Armleuchter-Algen galten lange Zeit als nächste Verwandte der heutigen Landpflanzen. Die aktuelle Studie zeigte, dass die oft einzelligen Zieralgen jedoch näher mit den Landpflanzen verwandt sind.
Bildquelle: © Christian Fischer/ wikimedia.org; CC BY-SA 3.0
Der „Kölner Algenzoo“ war dabei eine wichtige Quelle für die beteiligten Wissenschaftler. „Winzig kleine, nur unter dem Mikroskop sichtbare Algen werden in der wahrscheinlich größten Algensammlung der Welt in Köln kultiviert“, erklärt Prof. Dr. Michael Melkonian, Leiter des Algen-Teilprojekts vom Botanischen Institut der Universität zu Köln. „In diesen Algensammlungen versuchen Wissenschaftler, die gesamte Biodiversität der Algen abzubilden. Auf die öffentlich zugängliche Sammlung können Wissenschaftler aus aller Welt zugreifen“, so Melkonian weiter.
Gigantische Datenmengen müssen verarbeitet werden
Für ihre Studie isolierten die Wissenschaftler Ribonukleinsäuren (RNA) aus den Algen und ausgewählten Pflanzen und versendeten diese zu einem der weltweit größten Sequenzier-Zentren, dem BGI-Shenzen in China, wo die Gensequenzierungen durchgeführt wurden. „Für jeden Organismus haben wir bis zu 800 Gen-Transkripte analysiert“, so Prof. Melkonian. Dabei entstanden riesige Datenmengen, deren bioinformatische Analyse Wissenschaftler an mehreren Universitäten in den USA und Kanada übernahmen.
Um der Datenflut Herr zu werden, mussten die Forscher neue, bioinformatische Methoden entwickeln. „Die Datensets, die wir in dieser Studie analysiert haben, waren zu groß und zu komplex für unsere bisher verfügbaren statistischen Methoden. Daher haben wir neue Ansätze entwickelt, mit denen wir die Datenmengen präzise auswerten konnten“, erklärt der Bioinformatiker Tandy Warnow von der University of Illinois, USA.
Manchmal trügt der Schein
Die Arbeit hat sich gelohnt, denn vom „Eintausend Pflanzen-Transkriptomprojekt“ profitieren die Wissenschaftler gleich mehrfach: Einerseits konnten sie mithilfe von phylogenetischen Stammbäumen evolutionsbiologische Fragestellungen klären. So zeigte ihre Datenanalyse beispielsweise, dass Landpflanzen zwar evolutionsbiologisch betrachtet spezialisierte Grünalgen sind, aber nicht so nah mit einer bestimmten Gruppe der Grünalgen, den sogenannten Armleuchter-Algen, verwandt sind, wie bisher angenommen. „Armleuchter Algen wachsen auf dem Grund sauberer Gewässer. Sie ähneln den Landpflanzen in vielfacher Hinsicht, denn sie sitzen fest im Boden verankert und sie betreiben Photosynthese über kleine „Blättchen“, so Prof. Melkonian.
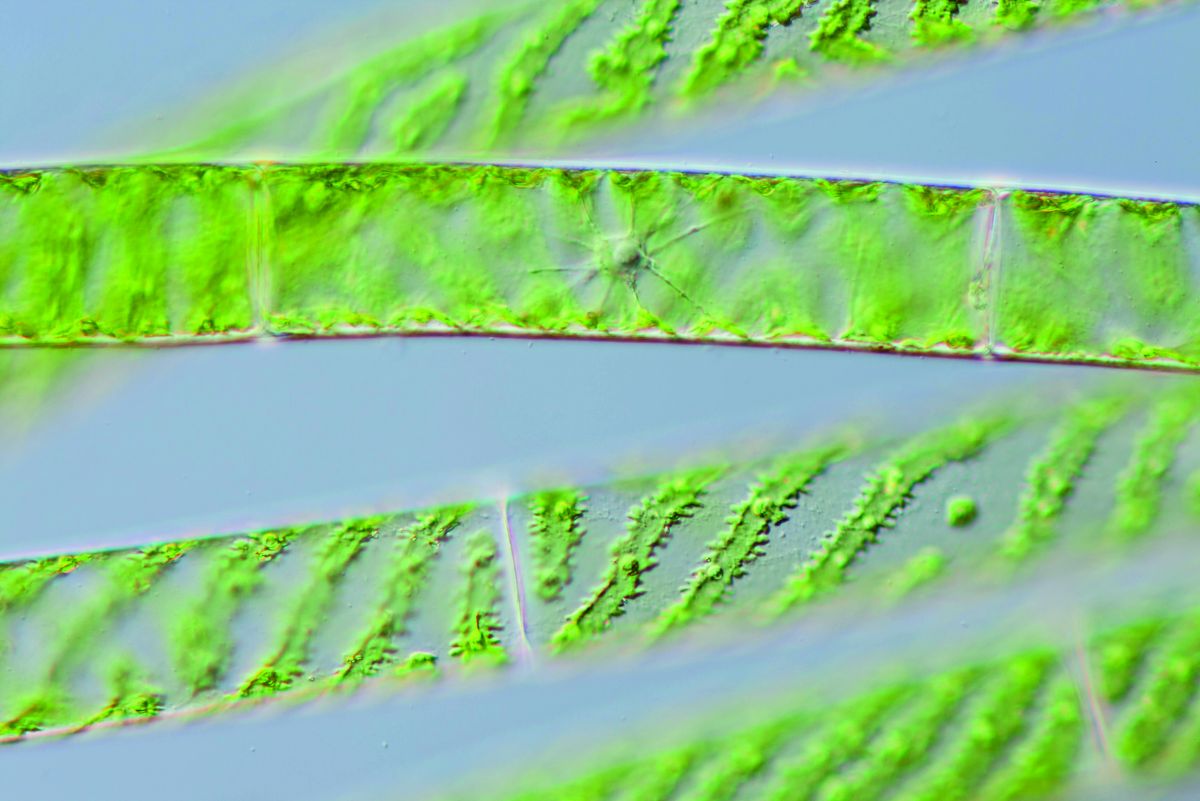
Die einfache, filamentöse Alge Spirogyra gehört zur Gruppe der Zieralgen. Der Chloroplast ist spiralförmig aufgewunden, weswegen sie auch als Schraubenalge bezeichnet wird.
Bildquelle: © Michael Melkonian, Universität zu Köln
Eine ähnlich komplexe Struktur lässt aber offenbar nicht immer auf einen nahen Verwandtschaftsgrad schließen. „Äpfel und Birnen sind sich ähnlicher als Äpfel und Pflaumen. Daher sind Äpfel enger mit Birnen verwandt als mit Pflaumen, das lehrt uns unsere Erfahrung“, veranschaulicht Melkonian. Für Armleuchter-Algen und Landpflanzen stimmt dieser Zusammenhang aber offenbar nicht. Die Analysen der Gentranskripte zeigte: Die einfach aufgebauten, oft einzelligen Zieralgen sind näher mit den heutigen Landpflanzen verwandt als die Armleuchter-Algen.
Noch mehr Gensequenzen für Forschungsprojekte
Auch an anderer Stelle profitieren Wissenschaftler weltweit vom „Eintausend Pflanzen-Transkriptomprojekt“: „Die Anzahl an pflanzlichen Gensequenzen hat sich durch dieses Projekt etwa verzehnfacht“, so Melkonian. Diese Daten können Forscher auf der ganzen Welt für vielfältige Projekte nutzen. Eines davon ist beispielsweise die Optogenetik. Dieses relativ junge Fachgebiet beschäftigt sich mit der Kontrolle von genetisch modifizierten Zellen mittels Licht. Alle Daten des „Eintausend Pflanzen-Transkriptomprojekts“ werden im Laufe des nächsten Jahres veröffentlicht werden.
Quelle:
Wickett NJ, et al. (2014): Phylotranscriptomic analysis of the origin and early diversification of land plants. In: Proc Natl Acad Sci U S A., (29. Oktober 2014 [Epub ahead of print]), doi: 10.1073/pnas.1323926111.
Weiterlesen auf Pflanzenforschung.de:
Titelbild: Lichtmikroskopische Aufnahme der einfachen, einzelligen Alge Netrium oblongum. Netrium oblongum gehört zur Gruppe der Algen, die am nächsten mit den heutigen Landpflanzen verwandt sind. (Bildquelle: © Michael Melkonian, Universität zu Köln)
